植物单细胞数据库PlantphoneDB——植物单细胞群体间的细胞交流
做植物单细胞测序的的朋友,可能都经历过这样一个时刻:拿到一份漂亮的t-SNE/UMAP图,细胞类型也注释好了,然后呢?下一个自然而然的问题就是——这些细胞之间,到底在怎么“聊天”?谁在发信号?谁在接收指令?哪个细胞类型是“发信人”,哪个是“收信人”?要回答这个问题,我们需要一套配体-受体(Ligand-Receptor)词典:告诉我哪些配体对应哪些受体,哪类细胞表达配体,哪类细胞表达受体,一匹配,通讯网络就出来了。
动物领域这方面的工具已经很成熟了,但轮到植物的时候,情况就有点尴尬,我们能用的专用资源,真的不多。厦门大学环境与生态学院郑海雷教授课题组通过对植物已知配体-受体互作进行挖掘和多个蛋白质互作数据库整合,专门为植物植物单细胞数据建立了一个植物单细胞受配体分析数据库PlantphoneDB[1]。
数据库主要包含单细胞数据集、L-R配对、R代码、测试结果等多个内容。均是开源的,有相关需求且能自己熟练运用R进行生信分析的老师可尝试自行分析对应。
【数据库介绍】
一 数据库网址
https://jasonxu.shinyapps.io/PlantPhoneDB/
二 适配物种
拟南芥、水稻、番茄、玉米、杨树
(其他物种可尝试利用同源比对来达到分析目的[2])


三 cell-cell communication结果展示
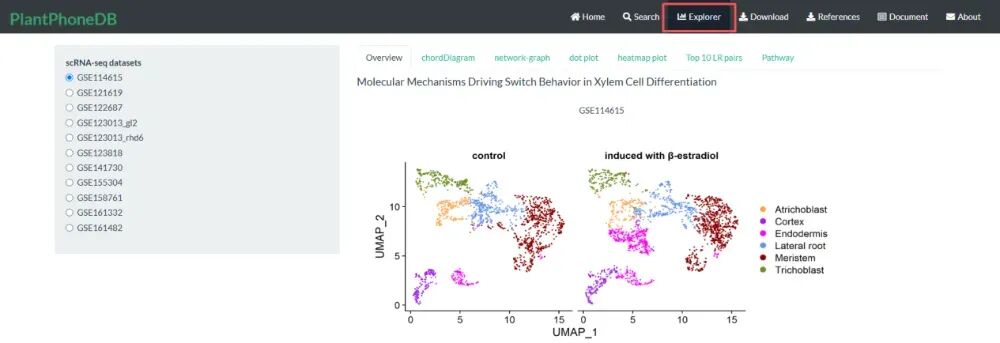
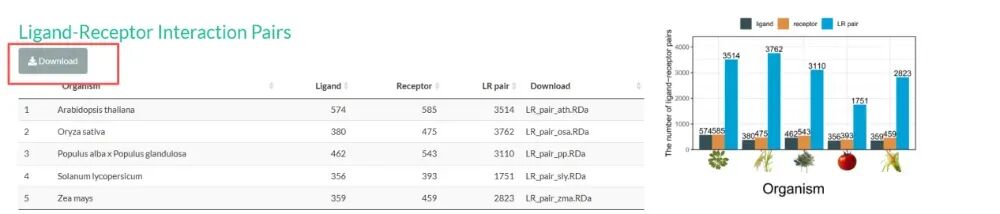
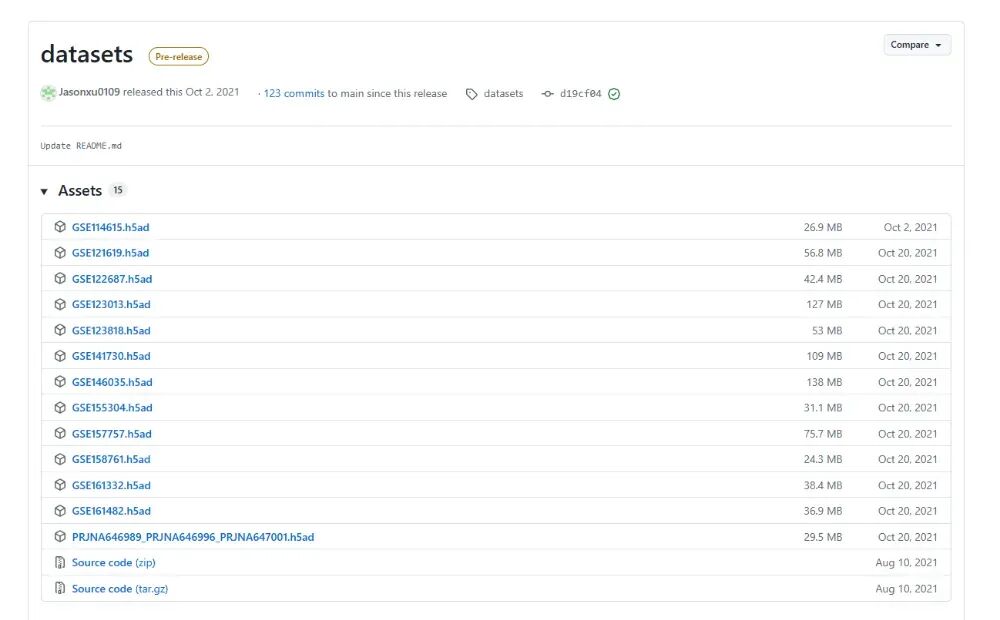
四 可供下载的5个物种的配体-受体相互作用对,以及可供测试的单细胞matrix
五 PlantPhoneDB使用指南(R代码的链接也在这里)
https://github.com/Jasonxu0109/PlantPhoneDB/blob/main/PlantPhoneDB-Tutorial/Case1.ipynb
【实测效果图】
数据集:GSE123013
物种:拟南芥
1. 细胞注释
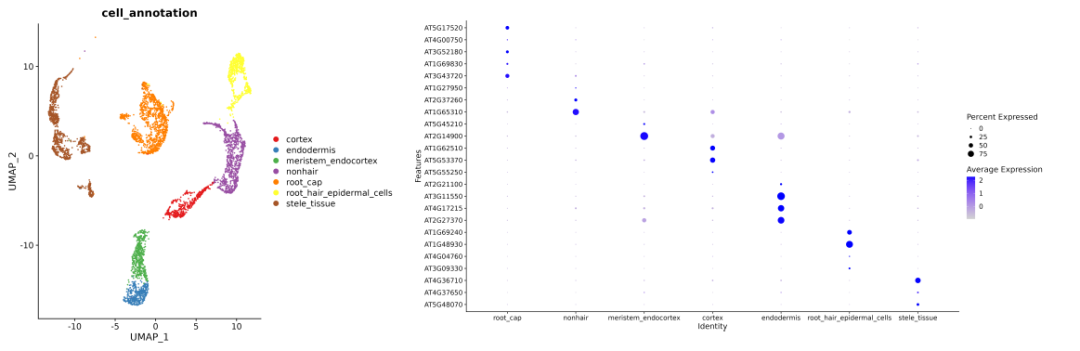
2. cell-cell communication结果解读
-
(1)通讯表格
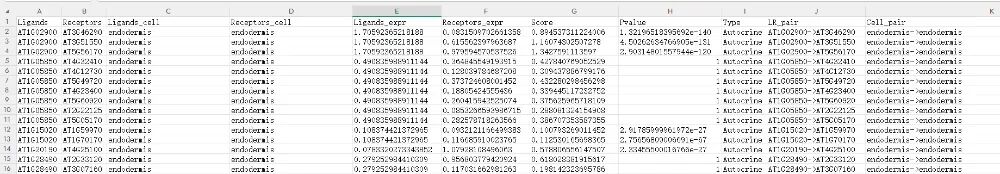
Ligands:配体基因(发送信号的基因)
Receptors:受体基因(接收信号的基因)
Ligands_cell:配体细胞群(配体所在的细胞类型)
Receptors_cell:受体细胞群(受体所在的细胞类型)
Ligands_expr:配体在发送细胞中的表达量(标准化后的数值)
Receptors_expr:配体在发送细胞中的表达量(标准化后的数值)
Score:细胞通讯强度综合评分,数值越高说明该互作越强
Pvalue:分析显著性
Type:Autocrine(自分泌);Paracrine(旁分泌)。根据信号的发送方和接收方是否为同一种细胞划分。
LR_pair:配体-受体基因对(LigandID-ReceptorID)
Cell_pair:细胞类型对(发送细胞-接收细胞)
-
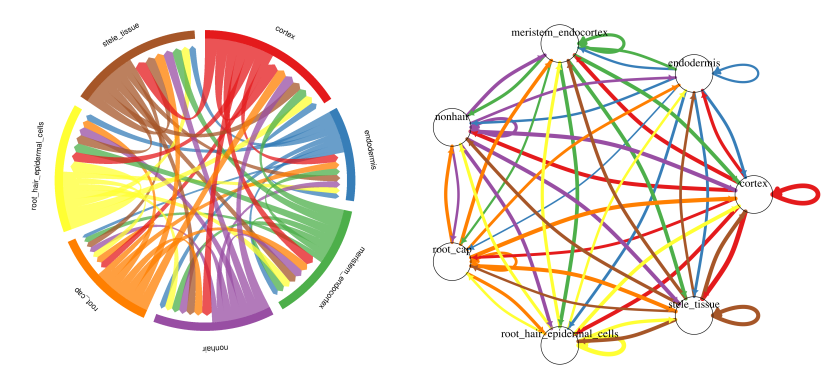
(2)细胞间通信的弦图(左)和circos图(右)
通过线条方向(箭头)和粗细描述细胞间的信号流向和强度
-
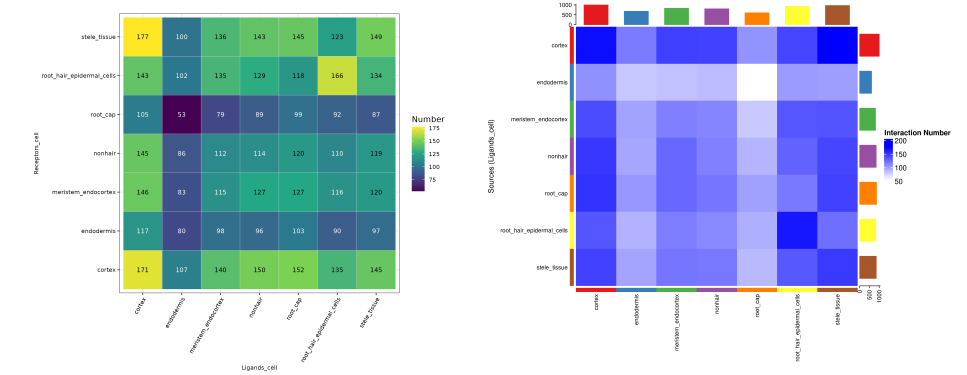
(3)cellSignaling_heatmap
左图是经典的标准交互计数热图,通过颜色和数字展示L-R互作数量;右图主要通过颜色展示L-R互作数量,在此之上,通过外侧柱状图展示每个细胞类型总共发出/接受的信号数,用于辨别整体的信号发送/接收枢纽。
-
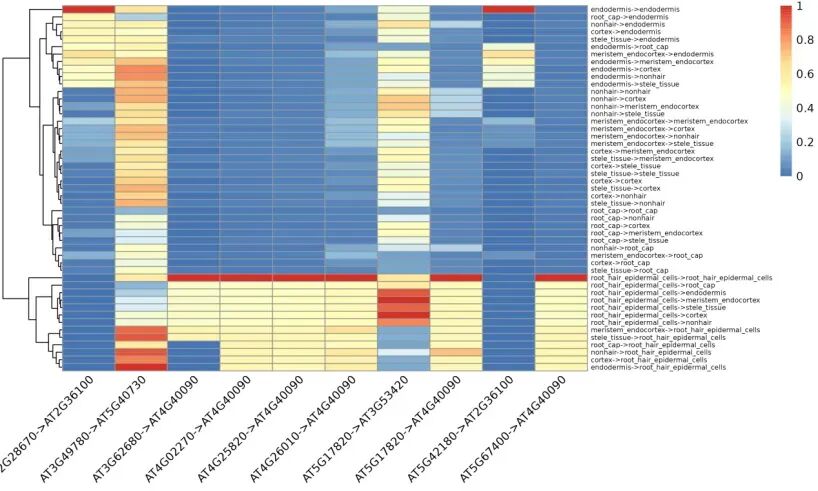
(4)top10_activity_heatmap
配体-受体互作的强度热图。强互作的L-R对和细胞对之间的特异性特征。
结 语
目前做植物的老师利用单细胞进行研究也已经是常态了,回到开头那个问题:拿到植物单细胞数据后,怎么分析细胞之间的“聊天记录”?PlantPhoneDB给出的答案是:把配体-受体词典备好,把表达数据放进去,通讯网络自然就出来了。本文的主要目的,就是把这个数据库介绍给更多做植物单细胞研究的朋友。它可能不是完美的,但它是目前少数专门为植物搭建的受配体分析资源之一——支持5个常见物种,有完整的R代码,有可直接测试的示例数据,上手门槛不算高。如果你也在做植物的单细胞项目,可以把PlantPhoneDB放进你的工具库里。
祝大家的单细胞数据,都能聊出好故事。
参考文献
[1] Xu, C., Ma, D., Ding, Q., Zhou, Y., and Zheng, H.-L. (2022) PlantPhoneDB: A manually curated pan-plant database of ligand-receptor pairs infers cell-cell communication. Plant Biotechnol J.
[2] Su H, Hu X, Meng L, et al. (2026) Time-series single-cell transcriptomics and spatial metabolomics reveal spatiotemporal tobacco leaf response to herbivory[J]. Journal of Advanced Research.
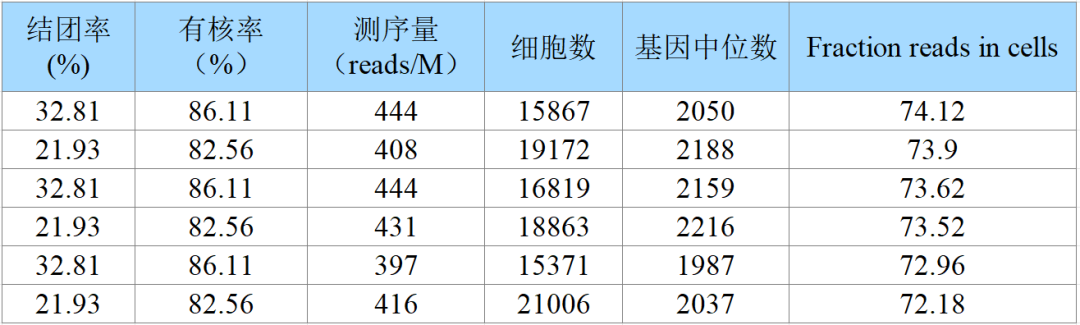
【爱基百客植物单细胞项目经验】
|
物种 |
组织部位 |
|
烟草,拟南芥,水稻,玉米,棉花,香蕉,橡胶,康乃馨,油菜,杨树,兰科,猕猴桃,牡丹,大豆等 |
根,花药,顶芽,果肉,花瓣,花柱,茎尖,胚珠,叶片,幼穗,种子,韧皮部,花粉等 |
实测数据

AtomGit 是由开放原子开源基金会联合 CSDN 等生态伙伴共同推出的新一代开源与人工智能协作平台。平台坚持“开放、中立、公益”的理念,把代码托管、模型共享、数据集托管、智能体开发体验和算力服务整合在一起,为开发者提供从开发、训练到部署的一站式体验。
更多推荐
 已为社区贡献4条内容
已为社区贡献4条内容






所有评论(0)