RM2Target v2.0:找RNA修饰靶点还在翻文献?这个引入AI大模型的数据库太有用了
在RNA甲基化修饰研究的火热浪潮中,Writers(书写器)、Erasers(擦除器)和 Readers(阅读器)——合称WER蛋白,无疑是主导调控机制的“三剑客”。
然而,搞清楚这些蛋白到底靶向了哪些基因?在特定细胞系中发挥了什么作用?与哪些疾病相关?往往需要耗费大量时间去浩如烟海的文献和高通量测序数据中“大浪淘沙”。
今天,我们介绍一个新的科研工具——RM2Target v2.0(中山大学研究团队开发)[1],它是一个RNA修饰调控蛋白的靶基因数据库。如果你正在进行RNA表观调控相关的课题,寻找下游靶基因、探索疾病分子机制,或者需要高质量的组学整合数据,RM2Target v2.0绝对值得关注和收藏。
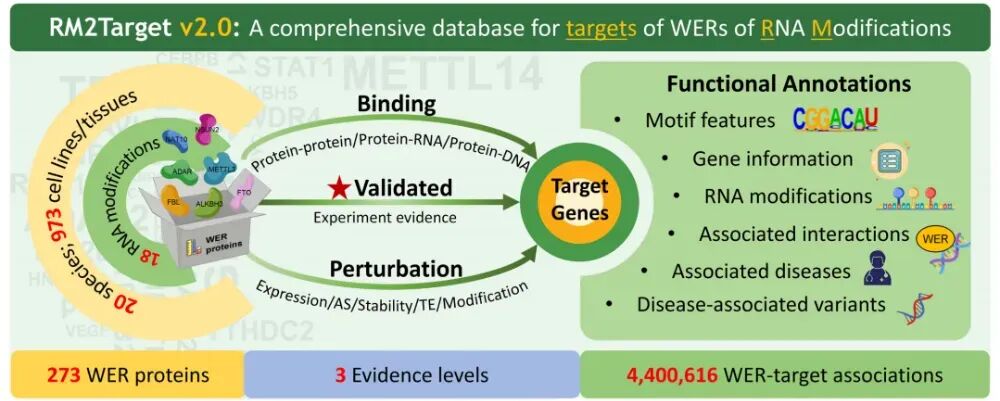
01 数据库研究的主角
在RNA修饰领域,有三类最核心的蛋白(统称为WER蛋白):
-
Writers(书写器):负责给RNA加上修饰(比如METTL3)。
-
Erasers(擦除器):负责把RNA上的修饰擦掉(比如FTO)。
-
Readers(阅读器):负责识别这些修饰并执行具体功能(比如YTHDF系列)。
这个数据库就是专门研究这三类蛋白究竟作用于哪些靶基因的。
02 数据库基本信息
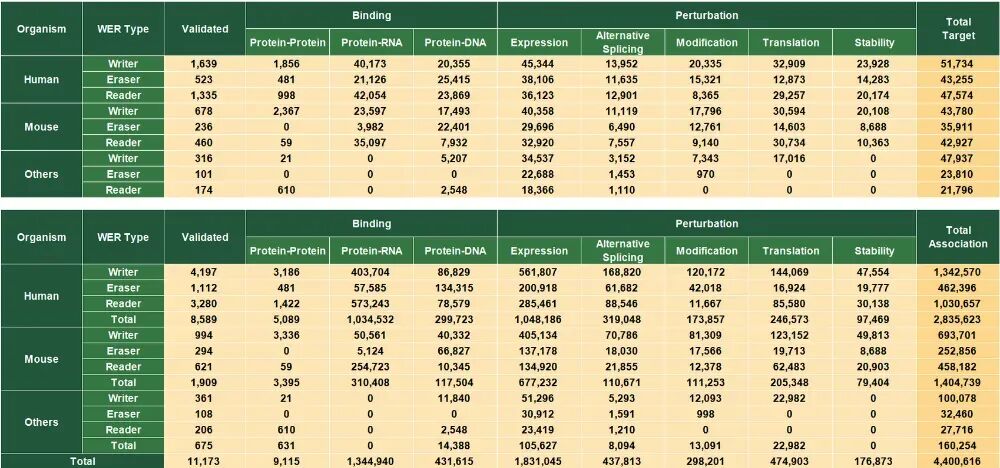
RM2Target是一个全面收录18种RNA修饰的书写器、擦除器和阅读器(WERs)靶标的数据库。研究团队收集了具有以下不同证据类型的靶基因:
-
已验证:通过3,388篇已发表文献中的WER扰动实验,验证了11,173个WER-靶标关联
-
结合:从CLIP-seq、RIP-seq、ChIP-seq和质谱等高通量测序数据中预测出1,785,670个具有结合证据的WER-靶标关联。
-
扰动:通过WER扰动后进行的RNA-seq、MeRIP-seq和Ribo-seq等高通量测序,推断出3,218,835个WER-靶标关联。总之,RM2Target收录了4,400,616个WER-靶标关联,涵盖20种生物(人、小鼠、拟南芥、线虫、斑马鱼、水稻等)中973种不同细胞系/组织的18种RNA修饰的273个WERs。
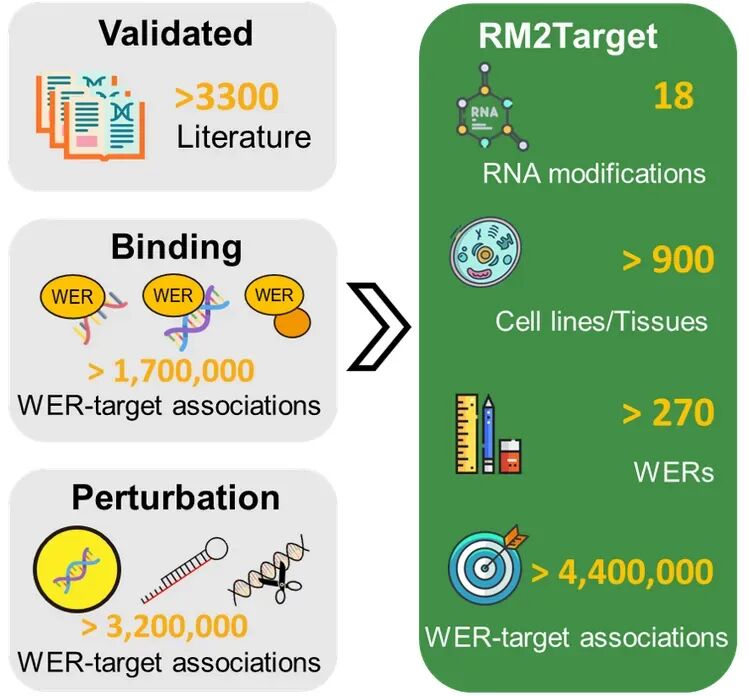
在RM2Target中,我们可以获取以下信息:
-
WER和靶基因的基本信息,如基因ID、基因符号、基因类型、别名和功能描述。
-
WER-靶基因关联的详细信息,如结合信息、检测方法、细胞系注释、扰动方向,以及在表达、翻译、可变剪接、稳定性或修饰水平上的下游效应。
-
靶基因的丰富注释,包括RNA修饰、RNA相关相互作用及相关疾病信息。
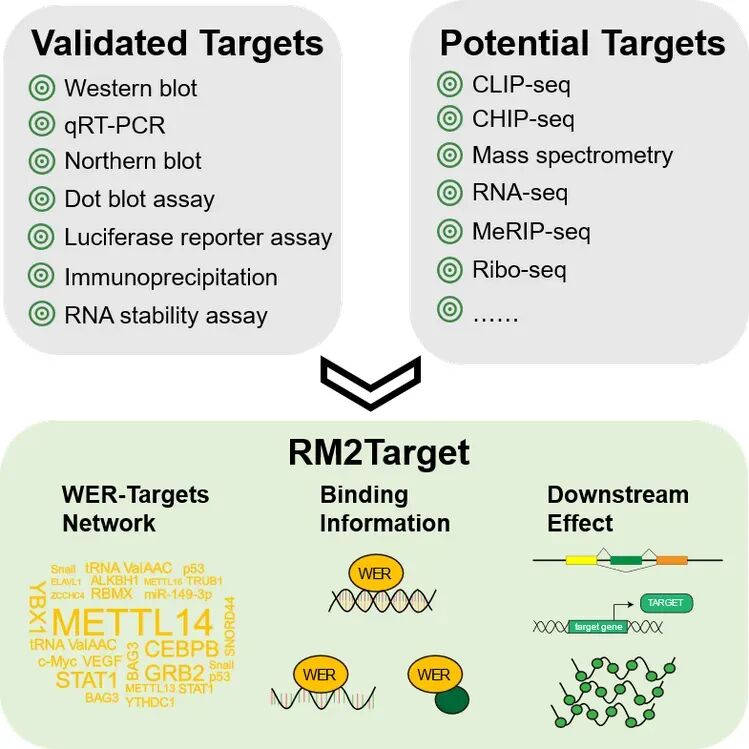
该数据近期升级到v2.0版本,此次数据库有几个升级亮点:
A. 数据量“狂飙”,涵盖20个物种的440万+互作
B. 大模型赋能,让数据整合更精准
这次升级最引人注目的技术亮点,在于团队创新性地采用了大语言模型(Large Language Models)来辅助人工审阅(Curation)。
C. 全方位深度注释,直击临床疾病与调控机制
对于科研人员来说,只知道“谁靶向谁”是不够的。RM2Target v2.0提供了极致丰富的多维注释信息:
-
修饰图谱 (Modification profiles):直观展示靶基因上的修饰位点分布。
-
分子互作网络 (RNA interactions):帮助你构建更庞大的分子调控网络。
-
临床疾病关联 (Disease links):数据库将靶基因与各类疾病进行了深度关联注释。
03 如何使用数据库?
网址:http://rm2target.canceromics.org/
RM2Target网站界面
首页可以直接输入信息,进行检索。

菜单栏有“Browse浏览”、“Search搜索”、“Download下载”、“Help帮助”等。其中,帮助部分有详细的数据库使用教程供用户使用。今天,我们重点关注“浏览”部分。

点击菜单栏Browse,弹出如下窗口信息:
-
Browser
-
WER Information
-
Top Target Gene of METTL16
-
Top Motifs Found in Target Genes
-
Distribution
-
Browse Result
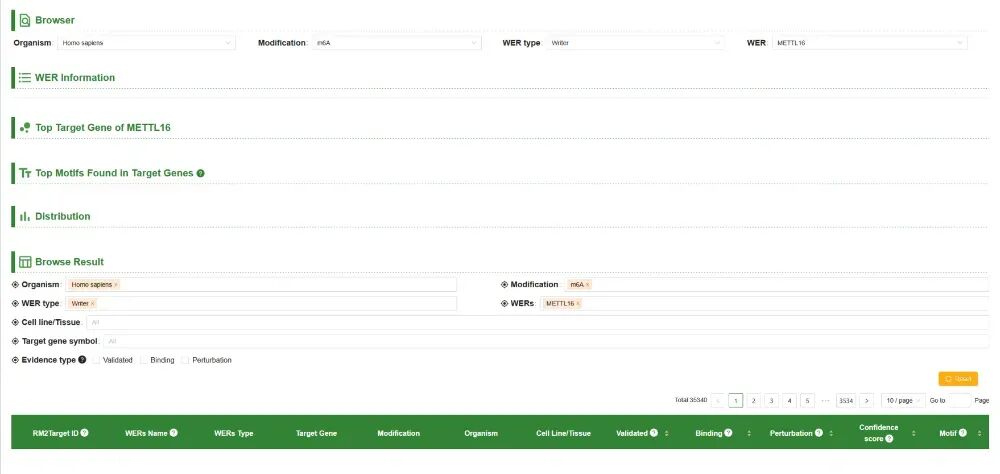
【1】Browser
第一栏有“Organism(选择物种,比如人、小鼠、拟南芥等)”、“Modification(选择修饰类型,比如m6A)”、“WER type(WER类型,比如Writer/Reader/Eraser)”、“WER(比如METTL16)”可供重新筛选。
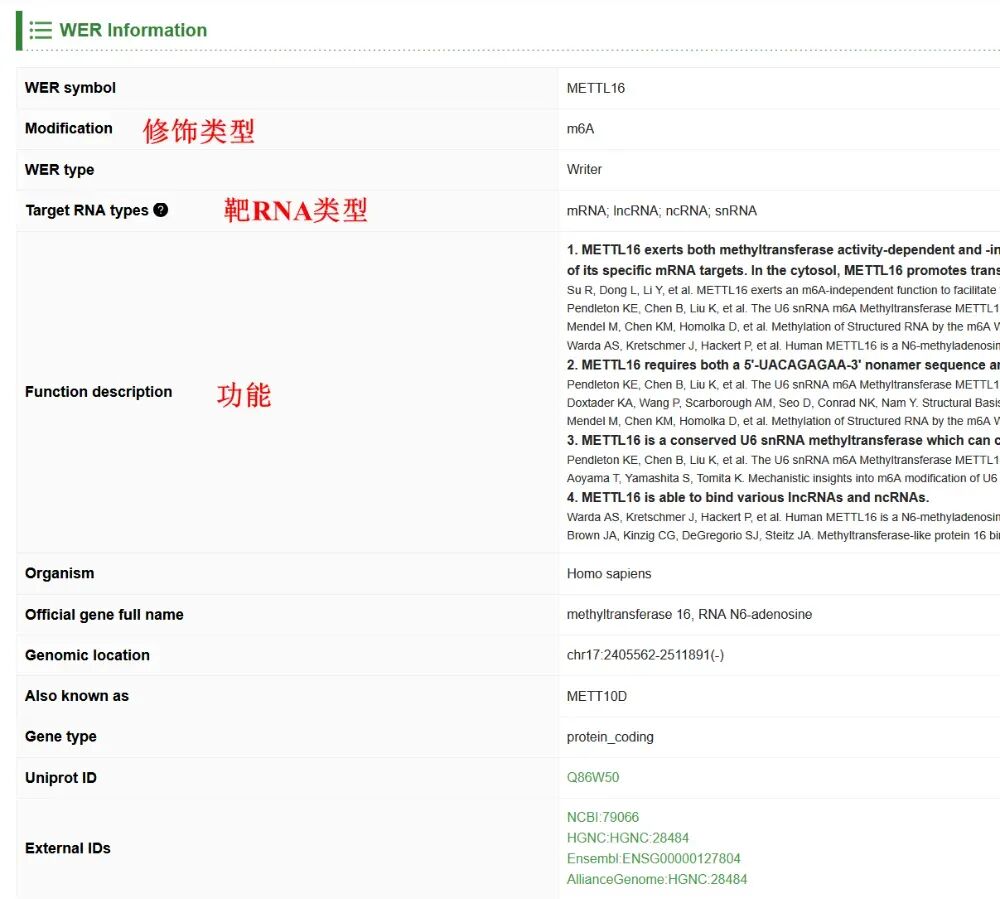
【2】WER信息
然后,可以看到WER的详细信息。其涉及WER符号、修饰、WER类型、靶RNA类型、详细功能描述等信息。
【3】靶基因词云
这里我们可以看到METTL16的靶基因词云,也可以选择可视化的数量。还可以点击靶基因的名字,查看具体的信息。

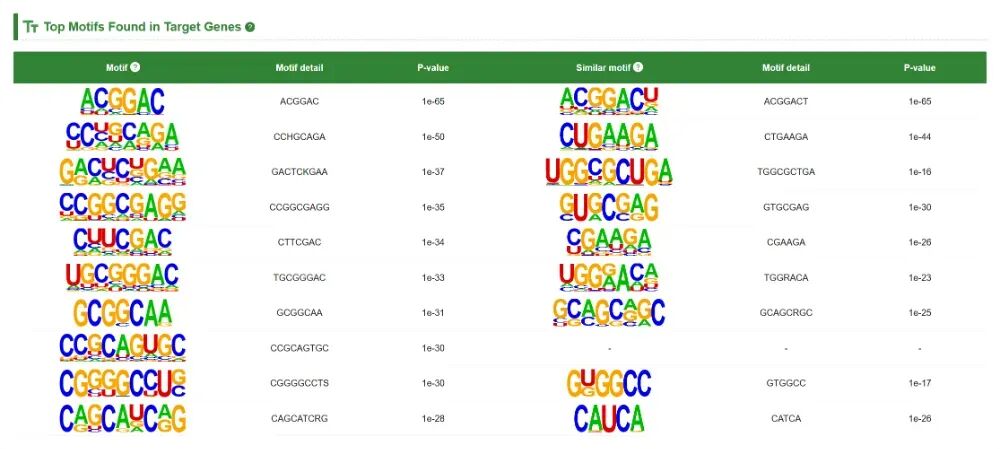
【4】靶基因motif
将来自Clip-seq或MeRIP-seq的相关峰作为输入,使用HOMER进行motif富集分析。
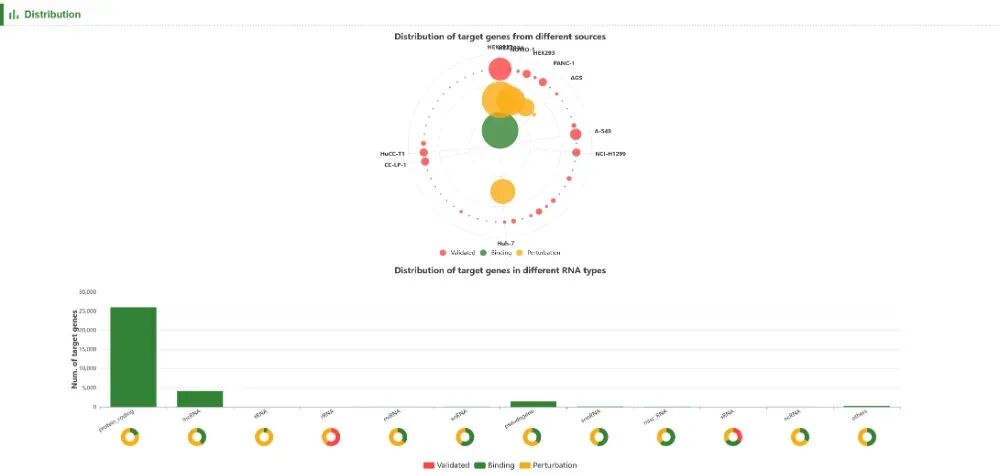
【5】靶基因分布
不同来源的靶基因分布。
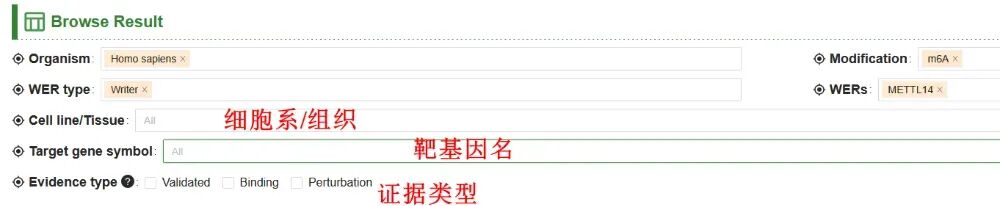
【6】筛选出来的查询结果
筛选出来的查询结果,可以重新筛选。此外,还添加了细胞系/组织类型、靶基因名和证据类型进一步筛选。
点击ID、Validated、Binding等来查看细节信息。
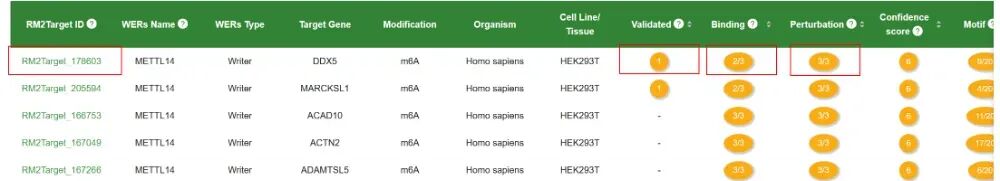
跳转的细节信息,我们可以看到如下信息:
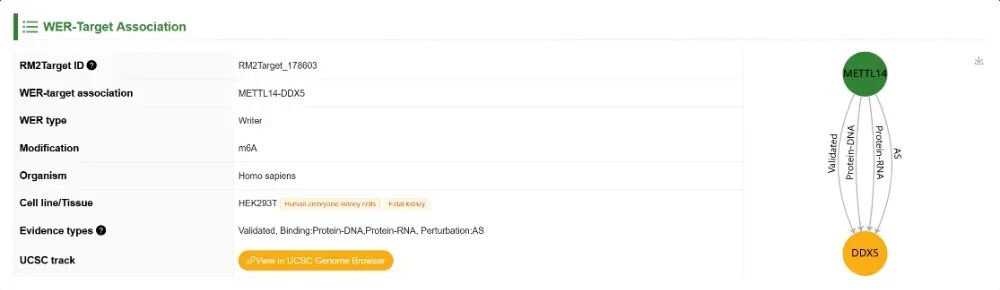
① WER-靶标关联
概括性信息,包括RM2Target ID、WER类型、修饰、生物体、细胞系/组织信息及相关证据类型。
② WER-靶标关联信息
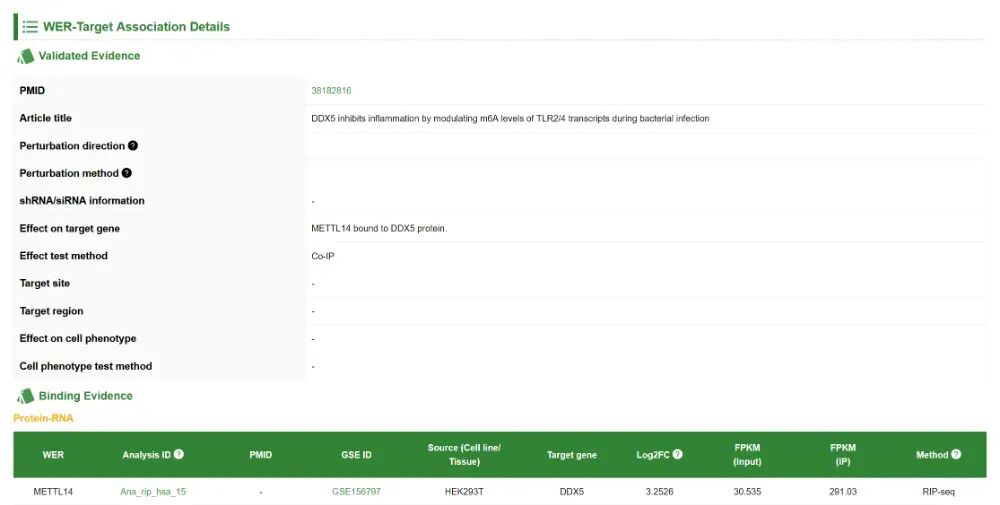
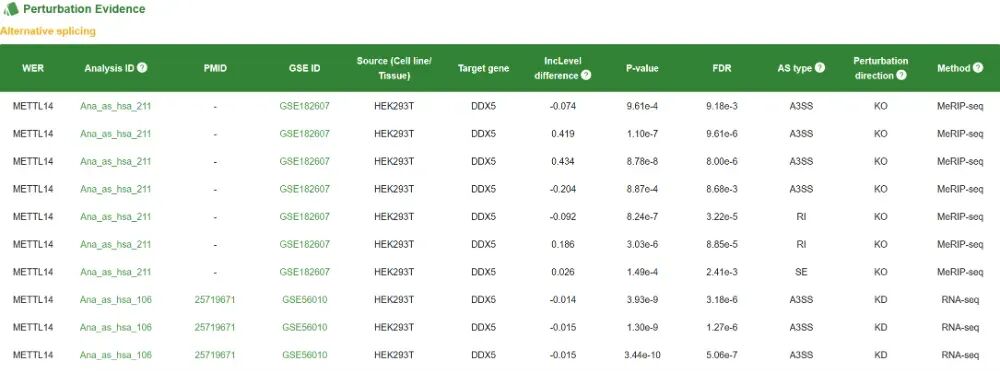
这部分内容包括“已验证的证据Validated Evidence”、“结合证据Binding Evidence”、“扰动证据Perturbation Evidence”。
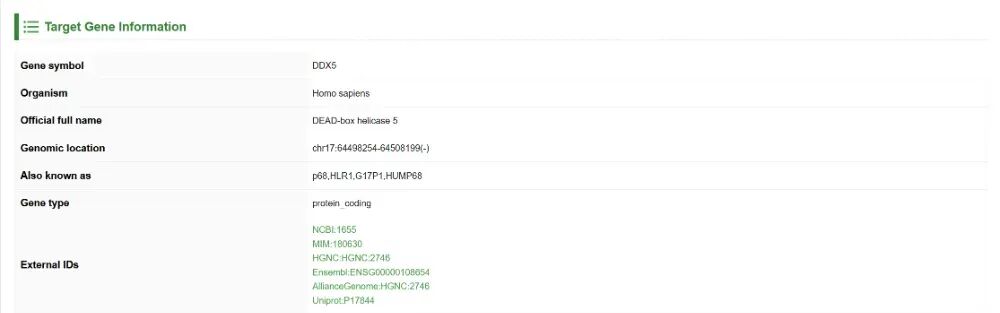
③ 靶基因信息
除了靶基因的基本信息外,这部分还提供了靶基因的注释,包括RNA修饰、疾病注释信息。
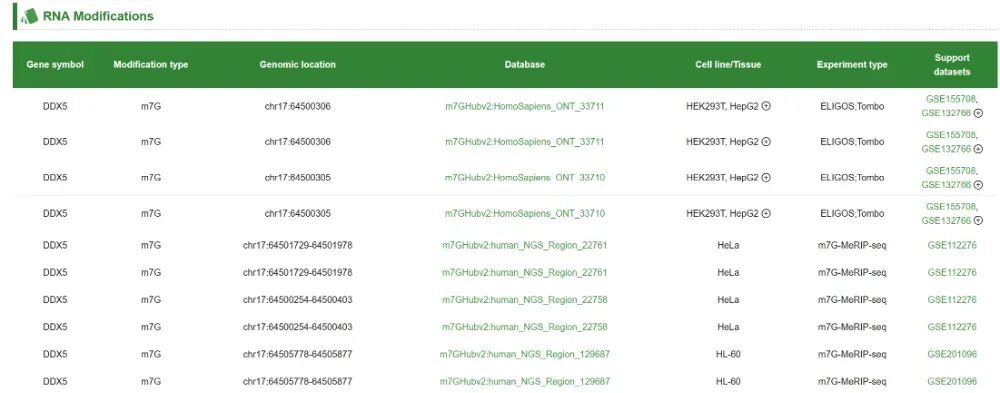
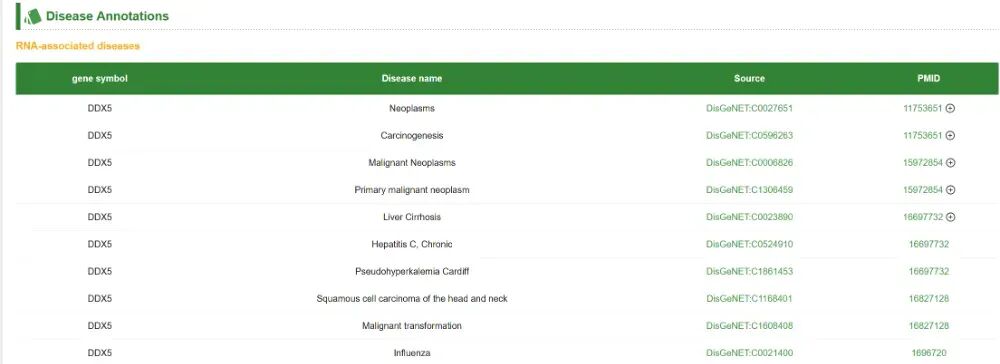
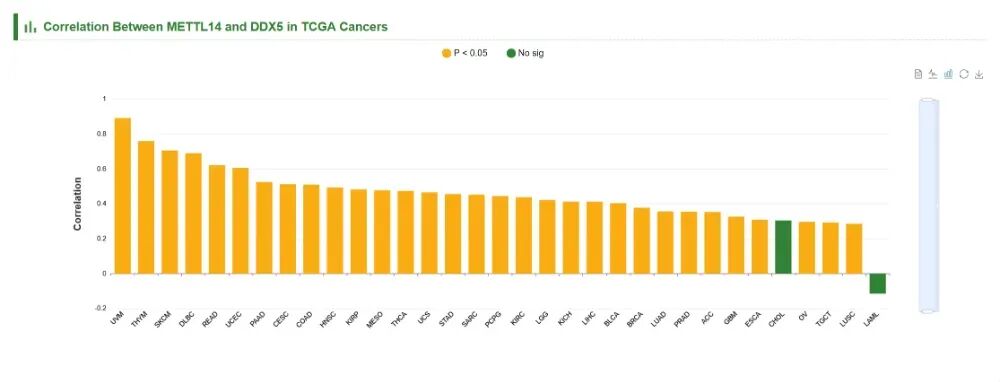
④ TCGA分析
这部分可以用于研究WERs表达与其靶点在癌症类型中的关联性。
今天的介绍就到这里了,更多关于数据库的使用欢迎自己摸索。如需做RNA修饰相关的技术服务,欢迎咨询~
-
参考文献
[1] Bao X, Jiang Q, Chen W, et al. RM2Target v2. 0: an updated database for the target genes of writers, erasers, and readers of RNA modifications[J]. Nucleic Acids Research, 2026, 54(D1): D279-D290.

AtomGit 是由开放原子开源基金会联合 CSDN 等生态伙伴共同推出的新一代开源与人工智能协作平台。平台坚持“开放、中立、公益”的理念,把代码托管、模型共享、数据集托管、智能体开发体验和算力服务整合在一起,为开发者提供从开发、训练到部署的一站式体验。
更多推荐
 已为社区贡献4条内容
已为社区贡献4条内容






所有评论(0)