【2026】PyMOL开源插件 让酶催化与蛋白结构研究提速的五个 PyMOL 插件:从构象优化、盒区提取到通道与口袋可视化 Optimize GetBox CAVER插件 PyVOL插件
PyMOL 不只是“看结构”:这 5 款优质插件,正在改变酶催化与蛋白结构研究的工作流
出处:智澈乐尚网络组工作平台
摘要
很多人第一次接触 PyMOL,只是把它当成一个“看 PDB 结构”的可视化软件。
但对于真正长期做酶催化、蛋白质结构分析、活性位点研究、分子对接后处理、蛋白工程设计的研究生和博士来说,PyMOL 的真正价值,往往不只在本体,而在插件生态。
像 PyMOL Optimize、PyMOL GetBox、CAVER、ParKVFinder-win、PyVOL 这几类插件,分别覆盖了分子结构预处理、对接 box 获取、蛋白通道分析、空腔检测、蛋白口袋可视化等高频科研需求。
它们不是简单让 PyMOL “多几个按钮”,而是在帮助科研用户把原本零散、重复、琐碎的结构分析动作,逐步串成更顺手、更高效、更适合表达的科研工作流。
对于做酶催化、酶工程、蛋白结构、生物信息交叉方向的同学来说,这类插件真正的意义,并不是“功能更花哨”,而是能把更多时间还给科研本身。
当然,这类插件普遍存在一个现实问题:安装和环境配置往往并不轻松,不是普通用户点几下就能稳定跑通的那种工具。
如果你也想把这类优质 PyMOL 插件真正落地到自己的科研流程中,这篇文章可以先带你做一个整体了解。
一、PyMOL 的真正上限,不在“会不会打开结构”,而在“会不会用插件”
如果你做的是蛋白质结构分析、酶催化、蛋白工程、分子对接、虚拟筛选或者相关的生物信息分析,那你大概率早就接触过 PyMOL。
它几乎已经成了很多科研用户的日常工具:
- 看蛋白整体构象;
- 看关键残基空间位置;
- 看配体、辅因子和蛋白的关系;
- 做结构图、答辩图、论文图;
- 做活性位点展示和结构解释。
但很多人用了很久 PyMOL,依然会觉得效率一般。
原因不是 PyMOL 不够强,而是只用到了最表层的功能。
因为在真实科研场景里,我们面对的往往不是“能不能打开结构”,而是更具体的问题:
- 这个小分子能不能先快速整理一下构象?
- 这个 docking box 怎么更快圈出来?
- 这个酶的底物进出通道到底通不通?
- 这个蛋白内部空腔能不能直观识别并定量描述?
- 这个口袋体积如何、是否存在 sub-pocket?
- 这些结果怎么更清楚地讲给导师、组会和审稿人听?
这时候,插件的意义就出来了。
插件不是给 PyMOL 做“装饰”,而是在给科研工作流做“加速”。
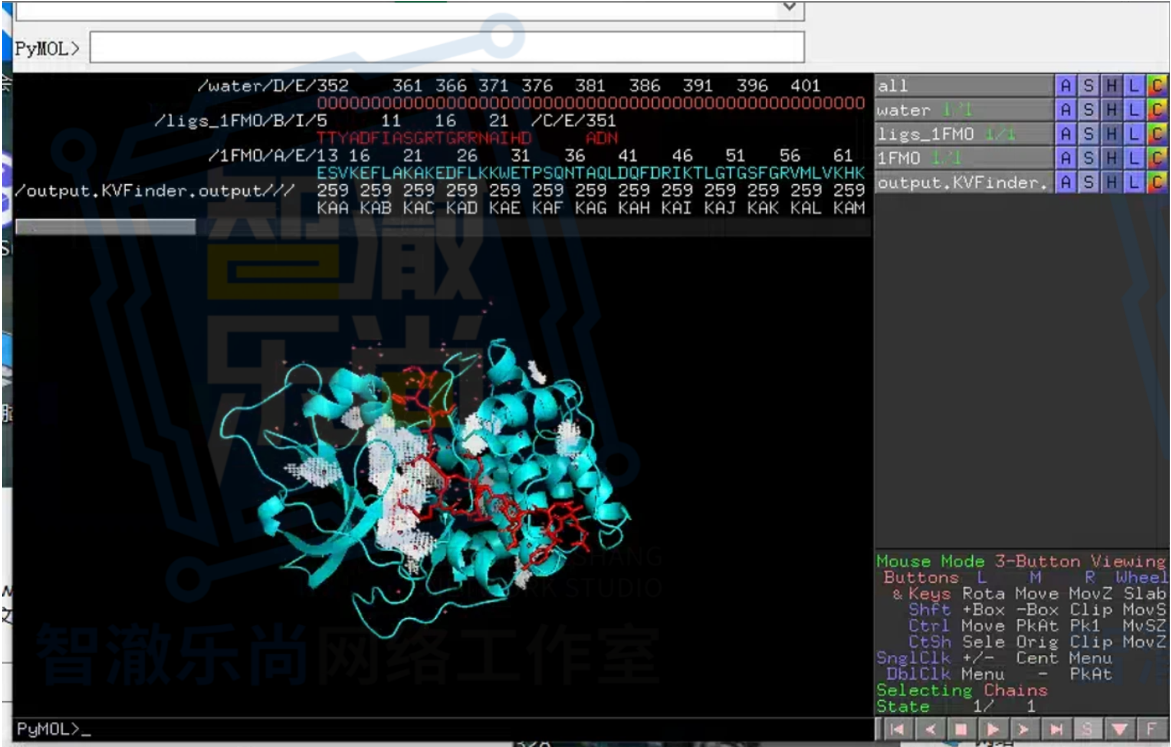
二、ParKVFinder-win:空腔检测,不只是“找洞”,而是帮助你更有条理地解释结构
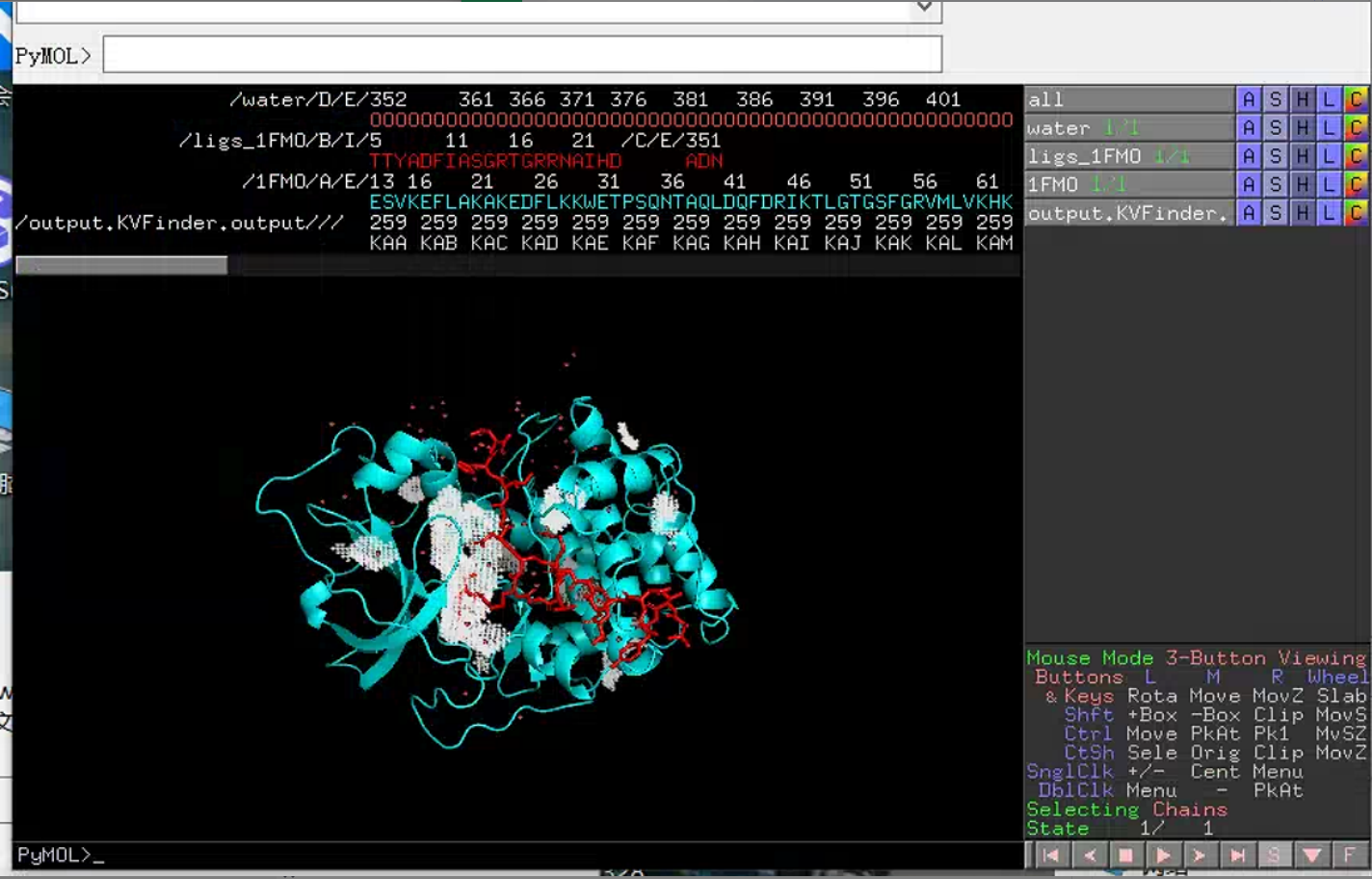
很多同学在看蛋白结构时,往往会有一种很常见的表达:
“这里好像有个 cavity。”
“这里看起来像个结合空间。”
“这个区域可能能容纳底物。”
这种判断当然有价值,但如果想把它变成更有条理、更有说服力的结构解释,就需要更进一步的工具。
这时候,ParKVFinder-win 这类空腔检测插件就非常重要。
它的作用,不只是“帮你找空腔”,而是帮助你从多个角度去理解这个空间对象,比如:
- 空腔位置;
- 空腔深度;
- 空腔边界;
- 空腔体积;
- 参与围成空腔的残基;
- 空腔的理化特征。
对于做酶催化、蛋白结构、生物大分子空间分析的人来说,这类信息很有现实意义。
因为在很多课题中,真正需要解释的不是“有没有 cavity”,而是:
- 这个 cavity 是否足够支持底物进入?
- 它在突变前后有没有变化?
- 它更偏向亲水还是疏水?
- 是否有进一步工程改造的潜力?
- 是否能作为结合位点、过渡空间或功能性区域来讨论?
一旦你开始把结构分析从“观察”推进到“解释”和“表达”,这类插件的价值就会非常突出。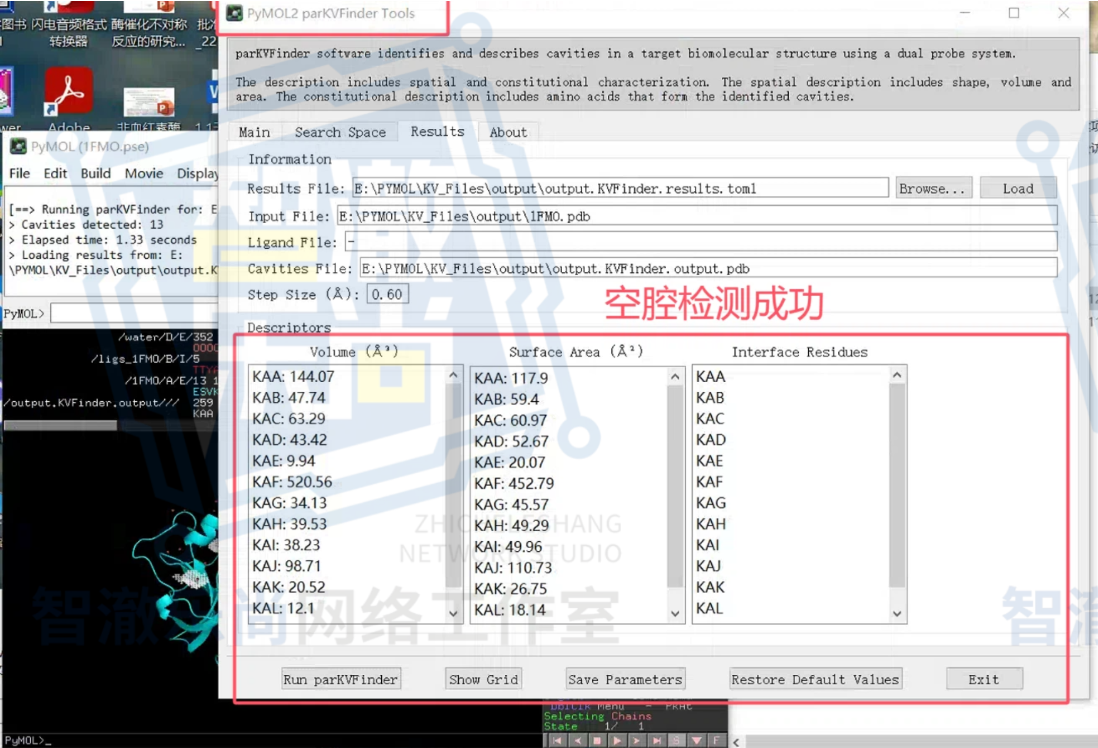
三、PyMOL Optimize:把分子结构预处理这一步做得更顺手
对于经常处理小分子、配体、底物、抑制剂或者初始构象的同学来说,PyMOL Optimize 是一个非常值得关注的插件。
它的核心意义,在于帮助用户在 PyMOL 环境里完成一部分基础分子结构优化或最小化处理。
这类能力对于很多做蛋白-配体分析的人来说非常实用,因为在真正进入后续分析之前,我们往往都希望先把结构处理得更规整一些、更自然一些、更适合观察和展示。
它的价值并不在于替代高精度的理论计算,而是在很多日常科研场景中,帮助你把一些“本来要切出去到别的软件里做的小动作”,尽可能直接在 PyMOL 里完成。
对于研究生和博士来说,这种小插件的好处其实非常直接:
- 节省来回切换软件的时间;
- 提高前处理效率;
- 让后续观察和作图更顺手;
- 降低小分子结构整理的操作成本。
很多工具的价值,不在于它有多“重”,而在于它能不能真正融入你的高频工作里。
Optimize 就是这种类型。
四、PyMOL GetBox:做分子对接前处理时,非常实用的一步
如果你做过分子对接,你就会知道,box 画得是否合理,往往直接影响后面的对接设置和效率。
而 PyMOL GetBox 这类插件的价值就在于:
它把“结构观察”和“对接准备”这两件事接起来了。
对于很多做酶催化、蛋白-配体相互作用分析、虚拟筛选前处理的人来说,最常见的问题之一就是:
- 这个 box 该围哪里?
- 是按配体中心来,还是按活性位点周围残基来?
- 范围要多大才合理?
- 怎么才能更快、更直观地确认对接区域?
如果完全靠手工估算和反复试错,不仅慢,而且很容易出现不必要的偏差。
而 GetBox 这类插件的优势就在于,它让你在已经熟悉的 PyMOL 结构环境里,直接完成对接 box 的获取和可视化确认。
这对于做酶催化和蛋白结构研究的同学来说,特别有帮助。
因为你在看结构的时候,本来就已经在关注:
- 活性口袋在哪里;
- 辅因子在哪里;
- 底物原始结合区域在哪里;
- 哪些残基是真正应该被覆盖进去的。
所以这类插件最实在的价值,就是把“你脑中的结构判断”快速转成“可用于对接设置的结果”。
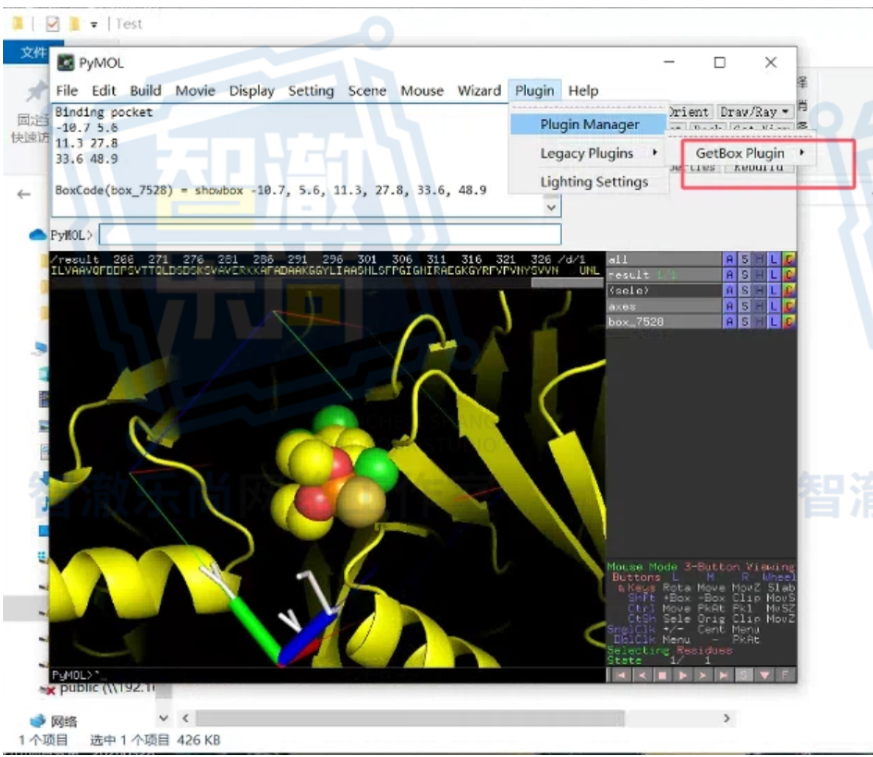
五、CAVER:做酶催化的人,很难绕开“通道”问题
在酶催化研究里,有一个非常容易被低估、但实际上又非常关键的问题,那就是:
底物怎么进去?产物怎么出来?通道通不通?瓶颈在哪里?
而 CAVER 这类插件,解决的正是这一层问题。
对于很多酶学研究来说,结构分析绝不仅仅是“盯着催化中心那几个残基看”。
真正决定催化效率、底物选择性、产物释放能力、抑制剂通达性甚至突变效果的,很多时候还包括:
- 蛋白内部是否存在合理的通道;
- 通道是否足够宽;
- 某些关键残基是否构成瓶颈位点;
- 不同构象下路径是否稳定存在;
- 突变后通道形状和可达性有没有变化。
这也正是为什么,做酶催化、酶工程、蛋白改造的人,一旦研究深入到一定阶段,几乎迟早都会认真看“通道分析”。
CAVER 的意义,并不是让你“多看一个结构特征”,而是帮助你把分析视角从“静态位点”拓展到“动态路径”和“结构限制因素”。
很多时候,这一步甚至会直接影响你后面对催化机制的理解和突变设计思路。
对于研究生和博士来说,这种工具的价值在于:
- 帮助你把问题看得更完整;
- 不只停留在口袋和位点层面;
- 让结构解释更接近真实的催化过程。
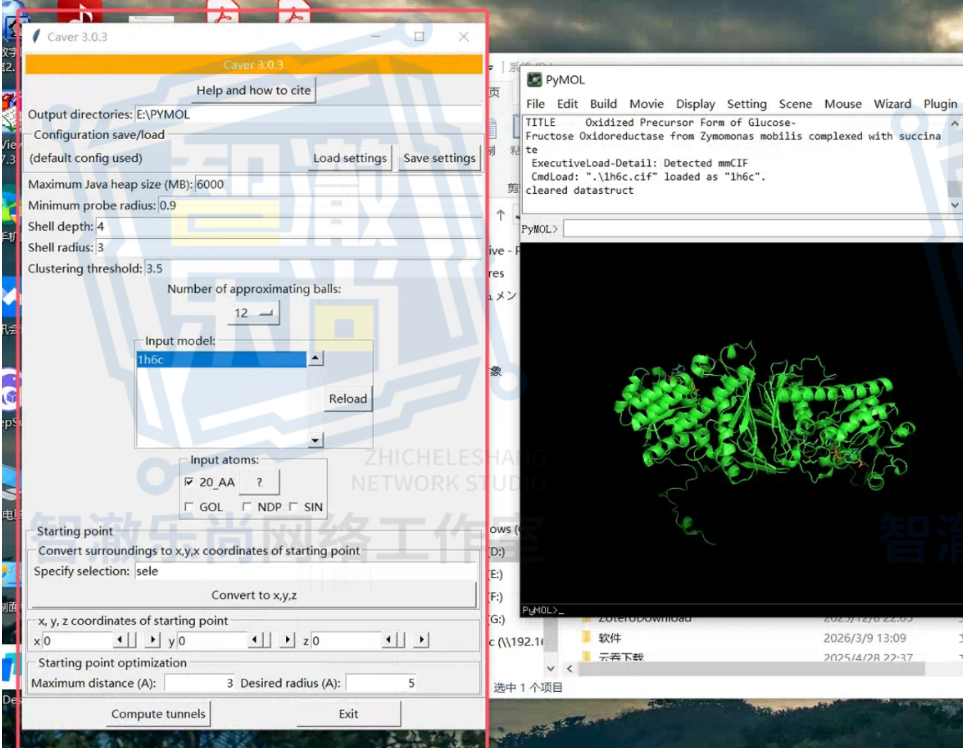
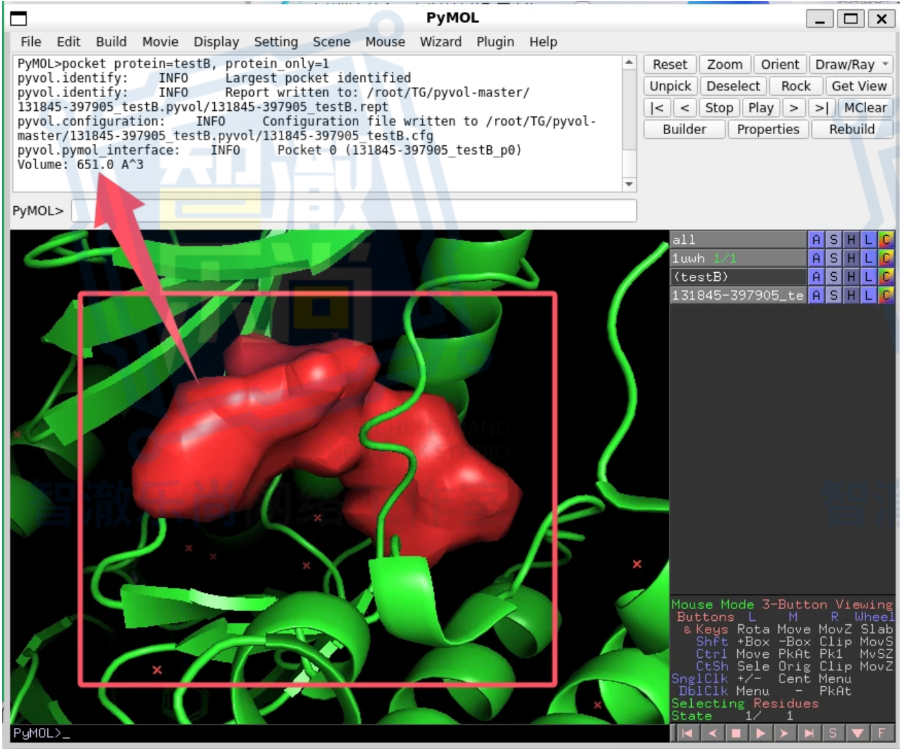
六、PyVOL:让蛋白口袋从“看起来像”变成“更清楚地讲出来”
在口袋分析这件事上,PyVOL 是一个非常有代表性的插件。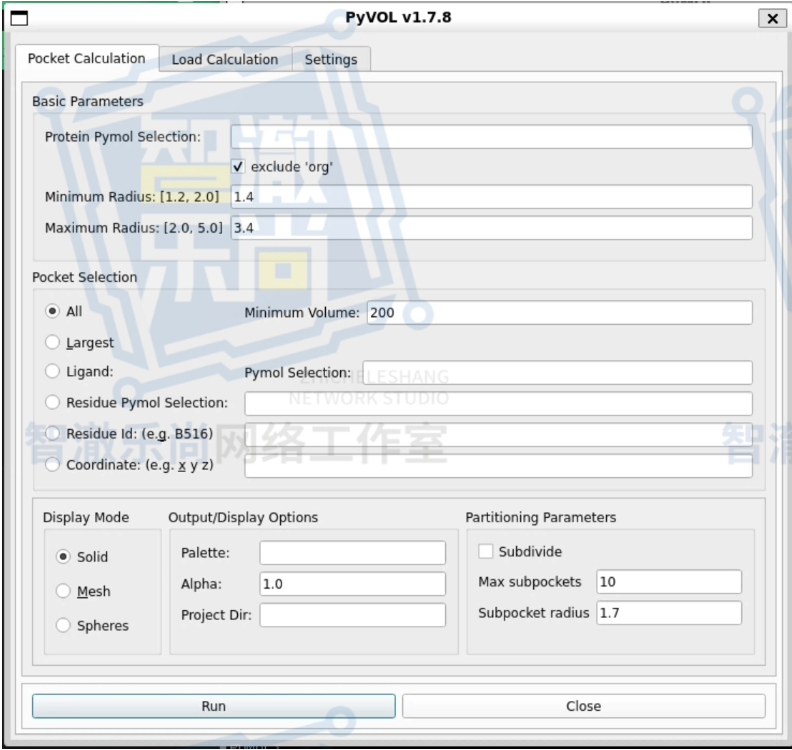
很多人平时都会说“这里有个 pocket”,但真正写汇报、写文章、做答辩的时候,仅仅说“有个口袋”其实远远不够。
你往往还需要回答:
- 这个口袋边界在哪里?
- 口袋体积大概如何?
- 是否可以划分为多个 sub-pocket?
- 不同构象之间口袋有没有明显变化?
- 它是否真的适合某类底物或抑制剂结合?
这时候,PyVOL 的价值就出来了。
它让口袋分析从一个“视觉印象”,逐渐变成一个更适合展示、比较和解释的对象。
对于做酶催化、蛋白-配体分析、蛋白工程和药物相关结构研究的人来说,PyVOL 的实用性非常高。
因为它不只是帮你“找到口袋”,而是帮助你把口袋这件事表达得更直观、更具体。
这对研究生和博士特别重要。
因为很多时候,科研并不只是你自己看懂了就结束了,而是你还要把这件事情讲给导师、组会、合作者、审稿人甚至答辩老师听。
而一个能够把 pocket 讲得更清楚的工具,往往会直接提升你的表达质量。
七、这 5 款插件真正改变的,不是某个功能,而是整条结构分析链
如果只单独看每一个插件,你会觉得它们各自只是解决了一个点:
- Optimize 偏向分子结构预处理;
- GetBox 偏向对接前 box 获取;
- CAVER 偏向通道和隧道分析;
- ParKVFinder-win 偏向空腔检测与表征;
- PyVOL 偏向蛋白口袋可视化和体积分析。
但如果把它们放在一起看,你会发现它们其实刚好对应了一条非常完整、非常实用的结构分析链:
结构观察 → 分子整理 → 口袋识别 → 空腔表征 → 通道分析 → 对接准备 → 结果表达
这也是为什么我认为,这几款插件非常值得推广。
它们并不是让 PyMOL “变复杂”,而是在帮助科研使用者把零散的结构分析动作,逐步组织成更顺手、更高效、更适合科研表达的工作流。
而对于做酶催化、酶工程、蛋白质结构方向的研究生和博士来说,这种工作流价值,往往比某一个单点功能本身更重要。
做酶催化和蛋白结构的人,真的值得早点建立自己的 PyMOL 插件体系
答案其实很现实:
不是不会用,而是经常卡在安装和环境。
这类插件普遍都有一个共同特点:
它们不是那种“下载下来点两下就稳稳能跑”的普通小工具。
很多时候,难点并不在“会不会用”,而在于:
- 系统环境是否合适;
- 图形界面依赖是否完整;
- Python 环境是否匹配;
- 第三方程序是否配好;
- 插件之间是否兼容;
- 不同平台下是否会有额外问题。
所以很多人不是不想把这些工具用起来,而是容易在真正落地那一步被劝退。
这也是为什么,能把这些优质 PyMOL 插件真正安装好、跑稳定、用顺手的人,后面在科研效率上往往会有明显优势。
如果你当前的研究方向涉及下面这些内容:
- 酶催化;
- 蛋白质结构分析;
- 活性位点研究;
- 酶工程与蛋白改造;
- 分子对接与虚拟筛选后处理;
- 蛋白口袋、空腔与通道分析;
- 论文图、汇报图和答辩图制作;
那么我个人是非常建议你尽早建立一套属于自己的 PyMOL 插件体系 的。
因为这些插件真正带来的价值,不只是“功能更多了”,而是让你在很多高频科研任务里:
- 更快上手;
- 更少试错;
- 更容易把结构看清楚;
- 更容易把结果讲清楚;
- 把更多时间花在真正重要的科研问题上。
对于研究生和博士来说,工具能力本身就是竞争力的一部分。
谁更早把这些优质工具真正落地到自己的科研流程里,谁往往就更容易在结构分析、结果表达和日常效率上拉开差距。
如果你对 PyMOL 插件生态、蛋白质结构可视化、活性位点分析、空腔检测、通道分析、蛋白口袋可视化 这类内容感兴趣,但又不想自己反复踩环境坑,欢迎进一步交流,博客:“智澈乐尚网络工作平台”。
如果你希望把这些优质工具更快落地到自己的科研流程里,也可以直接联系我沟通。

AtomGit 是由开放原子开源基金会联合 CSDN 等生态伙伴共同推出的新一代开源与人工智能协作平台。平台坚持“开放、中立、公益”的理念,把代码托管、模型共享、数据集托管、智能体开发体验和算力服务整合在一起,为开发者提供从开发、训练到部署的一站式体验。
更多推荐
 已为社区贡献3条内容
已为社区贡献3条内容






所有评论(0)