NPJ Precis Oncol 暨南大学附属第一医院放射科张斌等团队:基于生物可解释的多任务深度学习流程预测胶质瘤患者的分子改变、分级及预后
01
文献学习
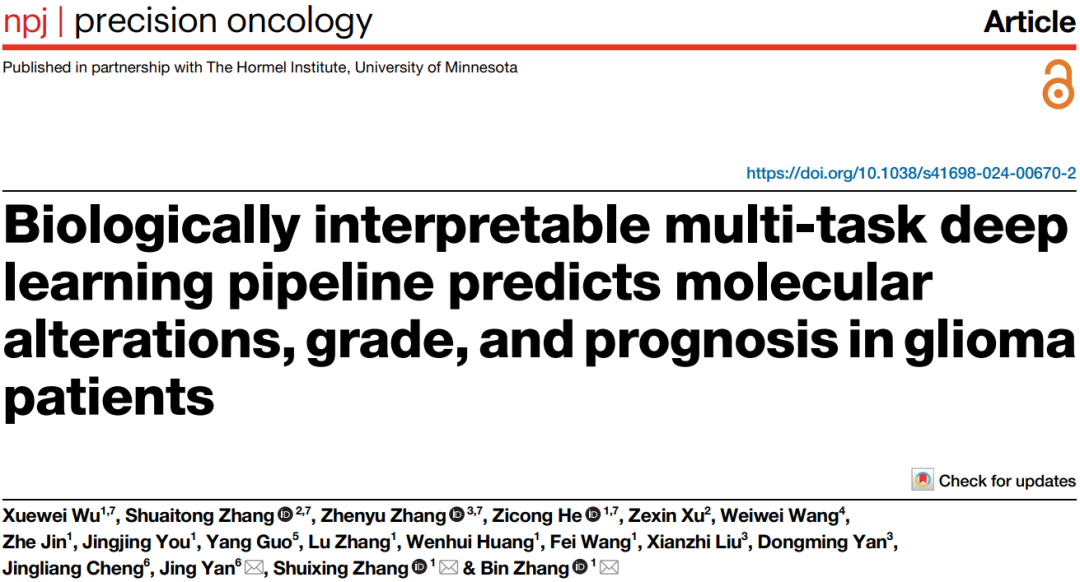
今天分享的文献是由暨南大学附属第一医院放射科张斌、郑州大学第一附属医院等团队于2024年8月在肿瘤学领域《npj Precision Oncology》(中科院1区top,IF=8)上发表的研究”Biologically interpretable multi-task deep learning pipeline predicts molecular alterations, grade, and prognosis in glioma patients“即基于生物可解释的多任务深度学习流程预测胶质瘤患者的分子改变、分级及预后,本研究开发了一个端到端的多任务深度学习(MDL)模型,仅基于诊断MRI图像,即可同时预测胶质瘤患者的分子特征(IDH突变、1p/19q共缺失)、组织学分级和预后,并通过多组学分析揭示其生物学基础,实现了非侵入性、全局性的个体化预后评估。
创新点:①首创多任务端到端深度学习模型,可同步预测胶质瘤分子改变、分级与预后,提升预测效率与集成性。②实现模型生物学解释性,通过多组学分析揭示影像特征与肿瘤微环境、免疫浸润等机制的关联。③引入自动肿瘤分割技术(mmFormer),减少人工干预,增强模型自动化与临床适用性。
临床价值:①非侵入性辅助诊断,基于MRI无创预测分子标志物与分级,减少活检依赖与手术风险。②实现个体化预后分层,通过DPS评分区分高低危患者,指导治疗决策与术后监测。③提供靶向治疗线索,结合多组学分析推荐潜在敏感药物,推动精准医疗实施。
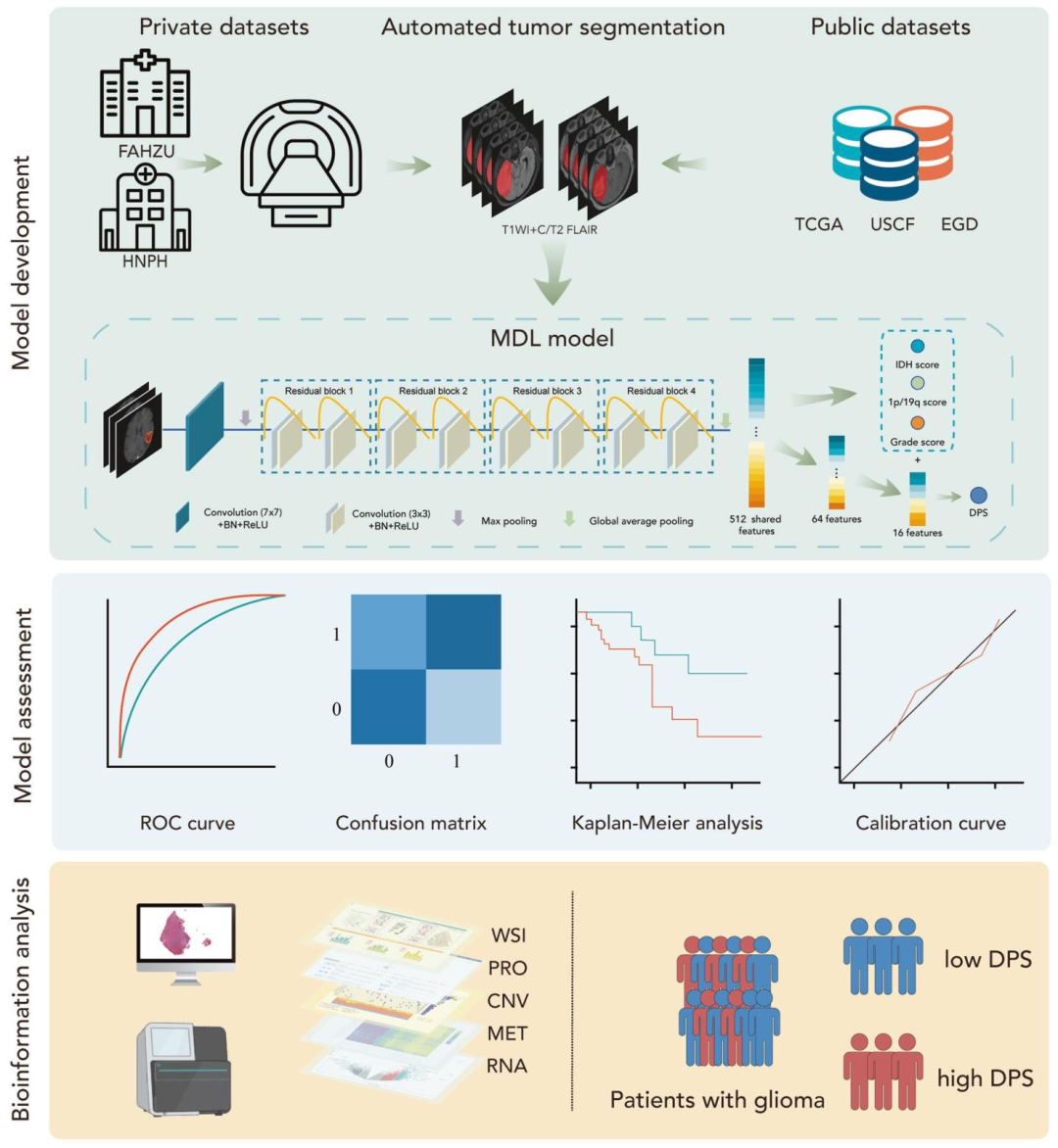
图 1:三阶段研究框架图
数据层面:明确私有数据集(FAHZU、HNPH)和公共数据集(TCGA、UCSF、EGD)的影像输入(T1WI+C/T2FLAIR);
预处理步骤:通过自动肿瘤分割(mmFormer)提取病灶区域;
模型架构:MDL模型共享512个特征,并行完成3个辅助任务(IDH状态评分、1p/19q状态评分、分级评分)和1个主要预后任务(DPS生成);
验证与解读:采用ROC曲线、混淆矩阵、Kaplan-Meier分析、校准曲线验证模型性能,结合多组学数据(WSI、PRO、CNV、MET、RNA)解析生物学机制。
02
研究背景及目的
研究背景
胶质瘤是高度普遍的脑肿瘤,作为全球癌症相关死亡的第三大原因,其临床诊断、治疗与预后评估亟需精准且高效的工具。2021年世界卫生组织(WHO)中枢神经系统肿瘤分类第五版提出了“整合诊断”新范式,强调同时结合组织病理学特征与分子基因型信息(如IDH突变状态、1p/19q共缺失状态、组织学分级等)进行综合判断,这些因素直接决定治疗方案选择与患者预后。然而,传统获取这些关键生物标志物的方法主要依赖侵入性组织活检或手术,不仅伴随采样误差风险,也难以实现动态监测。近年来,基于医学影像的深度学习模型在胶质瘤分析中展现出潜力,但现有方法大多受限于手动分割依赖、任务特异性设计(单任务模型)以及缺乏生物学解释性,限制了其临床转化与泛化能力。此外,医学影像人工智能的“黑箱”特性使其在治疗决策等高风险场景中的应用面临信任瓶颈,亟需建立影像特征与生物学机制之间的内在关联,以提升模型的可解释性与临床实用性。因此,开发一种能够同步预测多类临床指标、具备生物学可解释性且基于非侵入性影像的深度学习系统,成为当前胶质瘤精准医疗中的重要研究方向。
研究目的
本研究旨在构建并验证一个端到端、具有生物学可解释性的多任务深度学习(MDL)流程,仅使用诊断性MRI图像即可同时预测胶质瘤的分子改变(IDH突变、1p/19q共缺失)、组织学分级(WHO II/III级 vs. IV级)及患者预后(总生存期)。研究通过整合来自两个私有中心(共1931例)和三个公共数据集(共845例)的2776例患者多尺度数据,在内部与外部多个队列中进行严格训练与验证,以评估模型的稳健性与泛化性能。模型输出的核心指标——深度预后评分(DPS)用于将患者分为低风险与高风险亚型,并进一步通过放射多组学整合分析(包括转录组、蛋白质组、甲基化组、免疫浸润、肿瘤突变负荷等)系统揭示DPS背后的生物学基础,如致癌通路活化、免疫微环境特征、表观遗传改变等。最终,研究期望提供一个准确、非侵入性且具有明确生物学意义的辅助决策工具,不仅能实现分子分型与分级的高效预测(外部验证AUC最高达0.903),还能实现预后分层(C指数在独立队列中达0.723),并为不同风险亚型提示潜在靶向治疗策略,推动胶质瘤诊疗向个性化、全局化与机制驱动的方向发展。
03
数据和方法
研究数据
总样本量:2776例胶质瘤患者
数据来源:
私有数据集:FAHZU(1726例)、HPPH(223例)
公共数据集:TCGA(213例)、UCSF-PDGM(410例)、EGD(222例)
数据类型:基线MRI图像、分子标志物、生存数据、多组学数据(RNA-seq、甲基化、蛋白表达等)
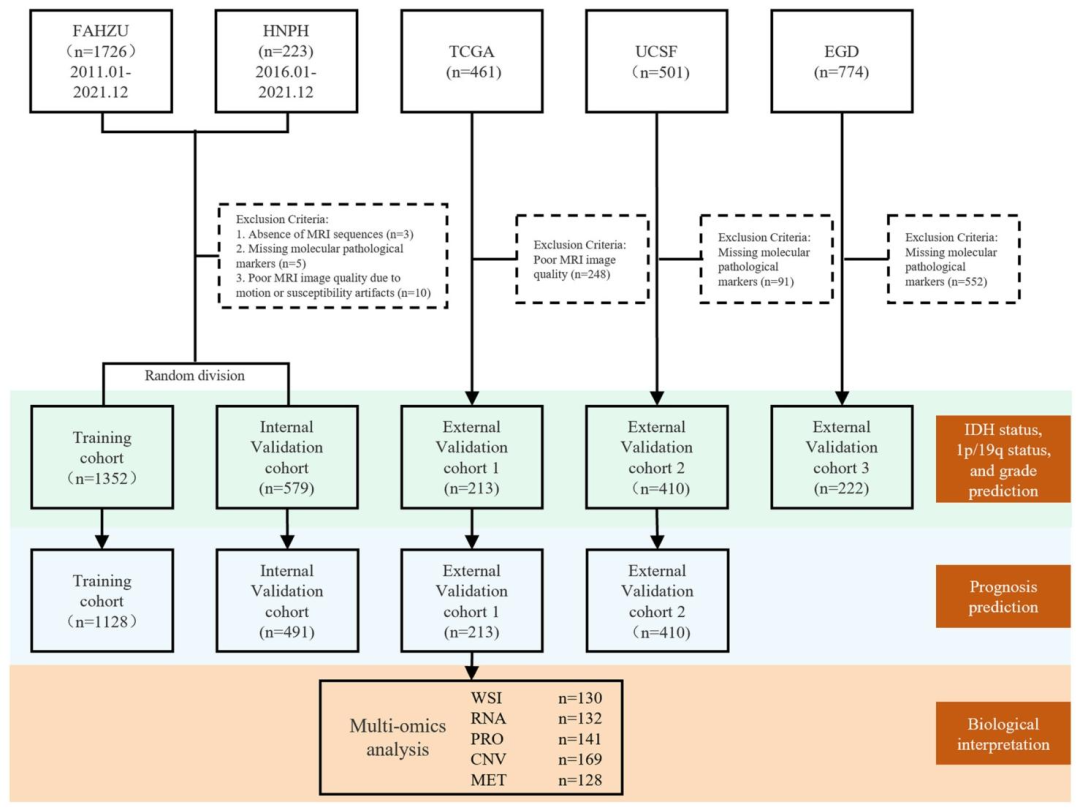
图 2:患者纳入与排除流程图
技术方法
图像处理:使用mmFormer进行自动肿瘤分割,并进行标准化和增强。
模型架构:基于3D ResNet-10构建多任务网络,共享特征层,分支出IDH、1p/19q、分级和预后预测任务。
训练策略:先训练三个分类任务,再冻结其参数训练预后任务(Cox损失函数)。
生物学解释:通过路径学、转录组、蛋白组、免疫浸润、甲基化等多组学分析,关联深度学习预后评分(DPS)与生物学表型。
04
实验结果
分类性能(外部验证):
IDH突变预测AUC:0.892–0.903
1p/19q共缺失预测AUC:0.710–0.894
肿瘤分级预测AUC:0.850–0.879
预后预测性能:
TCGA队列C指数:0.723
UCSF队列C指数:0.671
DPS与生物学特征相关:
高DPS组肿瘤-间质比例更低,免疫浸润更活跃,突变负荷更高。
高DPS组与EMT、血管生成、缺氧等通路激活相关。
高DPS组EGFR/HER2表达升高,低DPS组ERK2表达升高。
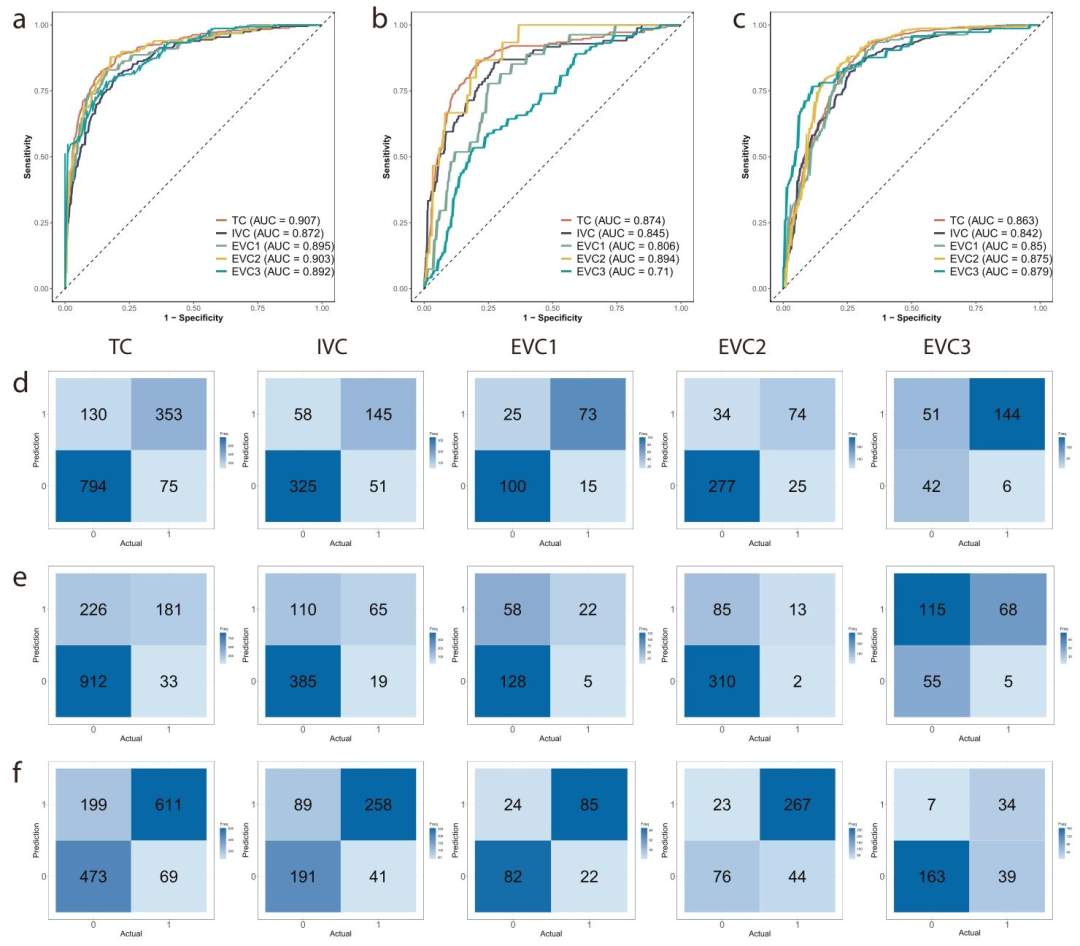
图 3:分子改变与组织学分级预测性能图
a- c 分别为预测IDH突变状态、1p/19q共缺失状态和组织学分级的受试者工作特征(ROC)曲线。d- f 为相应的混淆矩阵,展示两两比较结果;对角线:正确分类的病例数;非对角线:错误分类的病例数。
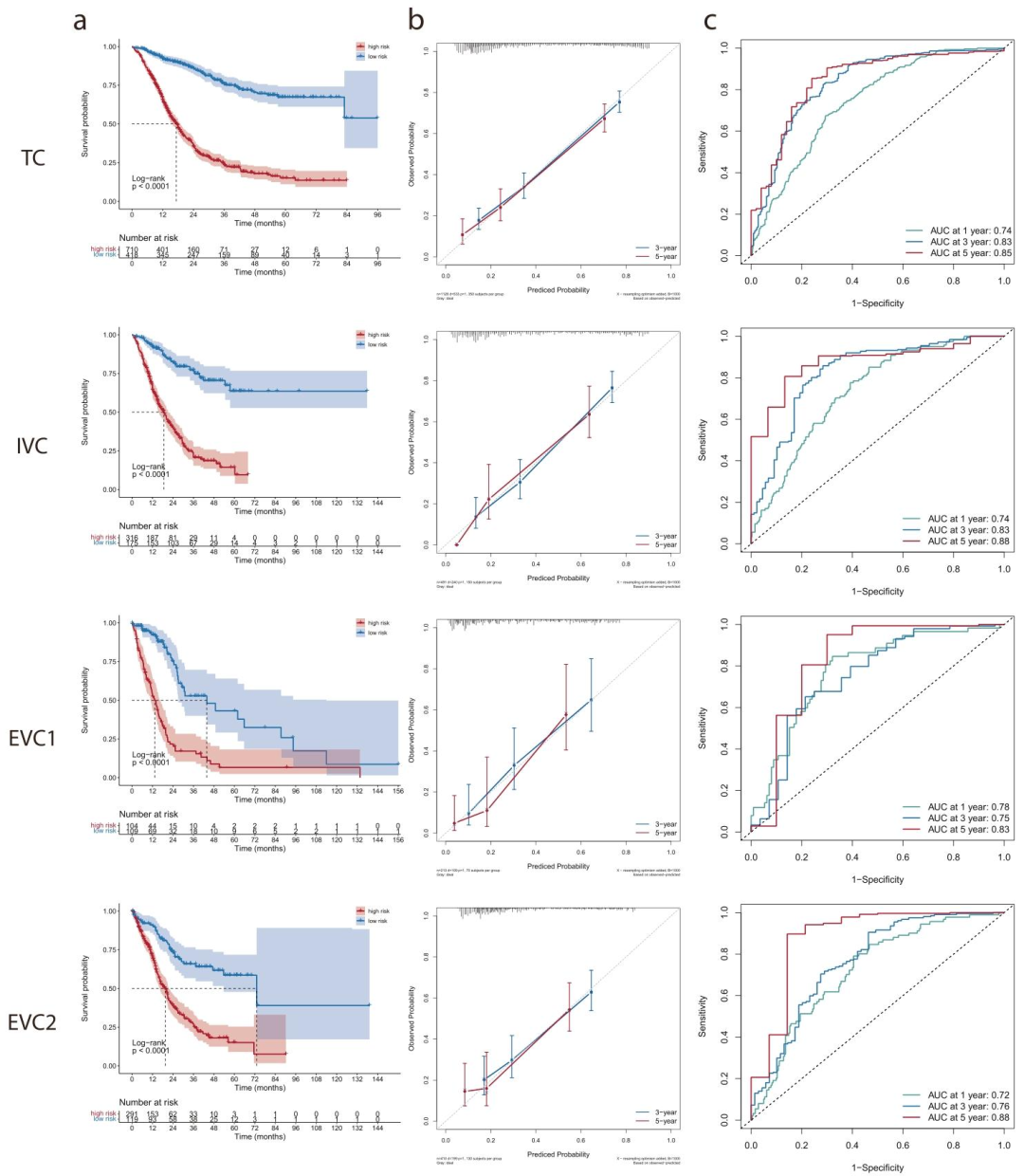
图 4:患者预后预测性能图
a Kaplan-Meier生存曲线展示低DPS亚型和高DPS亚型患者的总生存期(OS)。在训练集和验证集中,高DPS组患者的总生存期显著短于低DPS组。b 校准曲线展示实际生存概率与预测生存概率的一致性。c 1年、3年和5年时间节点的时间依赖型受试者工作特征曲线。
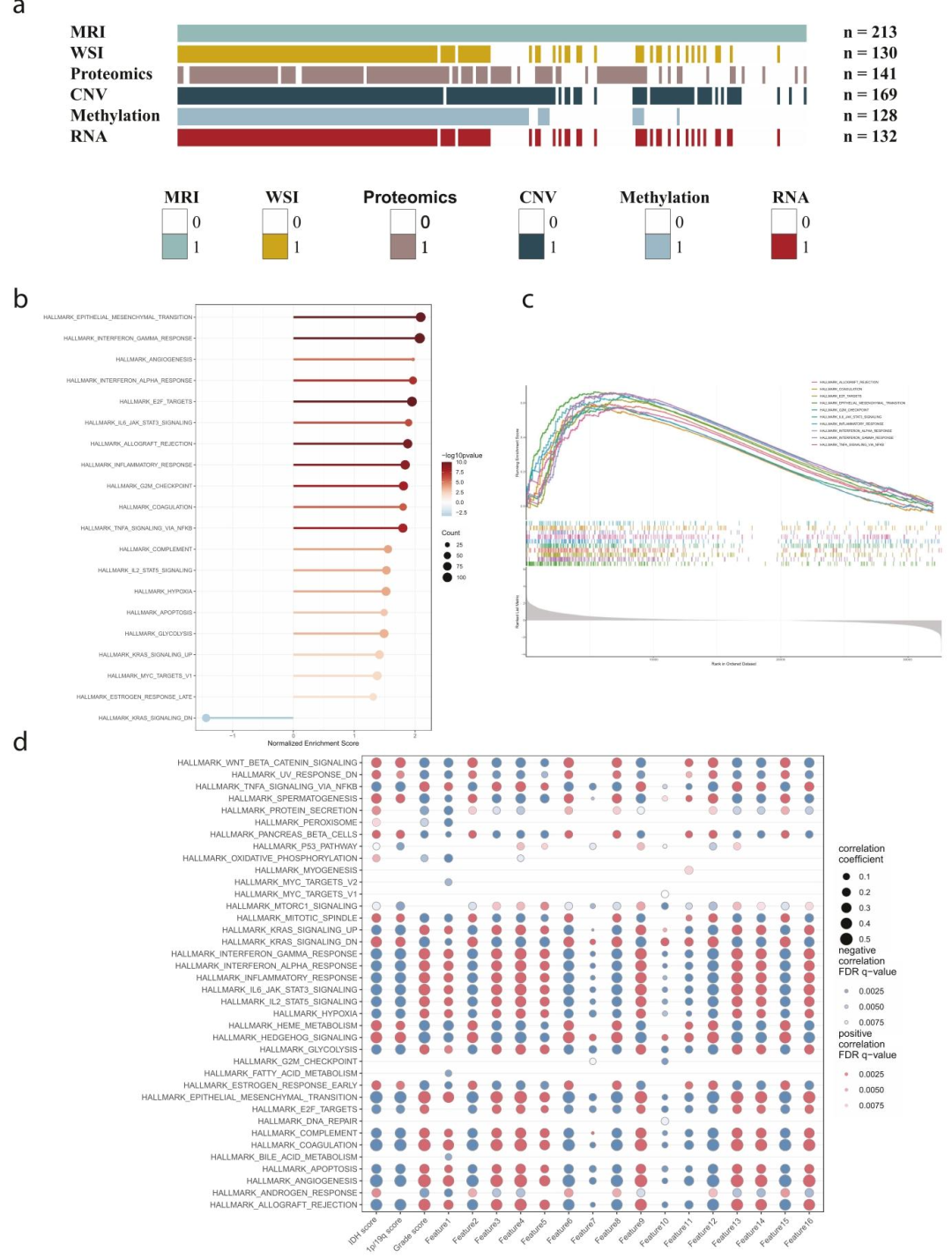
图 5:DPS在胶质瘤中的分子相关性图
a EVC1放射组学-多组学队列的队列信息,提供EVC1中匹配的多组学数据详情。每一列代表1例病例,彩色列表示该病例具备对应的多组学数据。b 按标准化富集分数排序,展示高DPS亚型(红色)和低DPS亚型(蓝色)中富集的主要通路。c 基因集富集分析(GSEA)用不同颜色展示显著富集的通路。d 气泡图展示预后深度特征与肿瘤生物学过程的相关性。
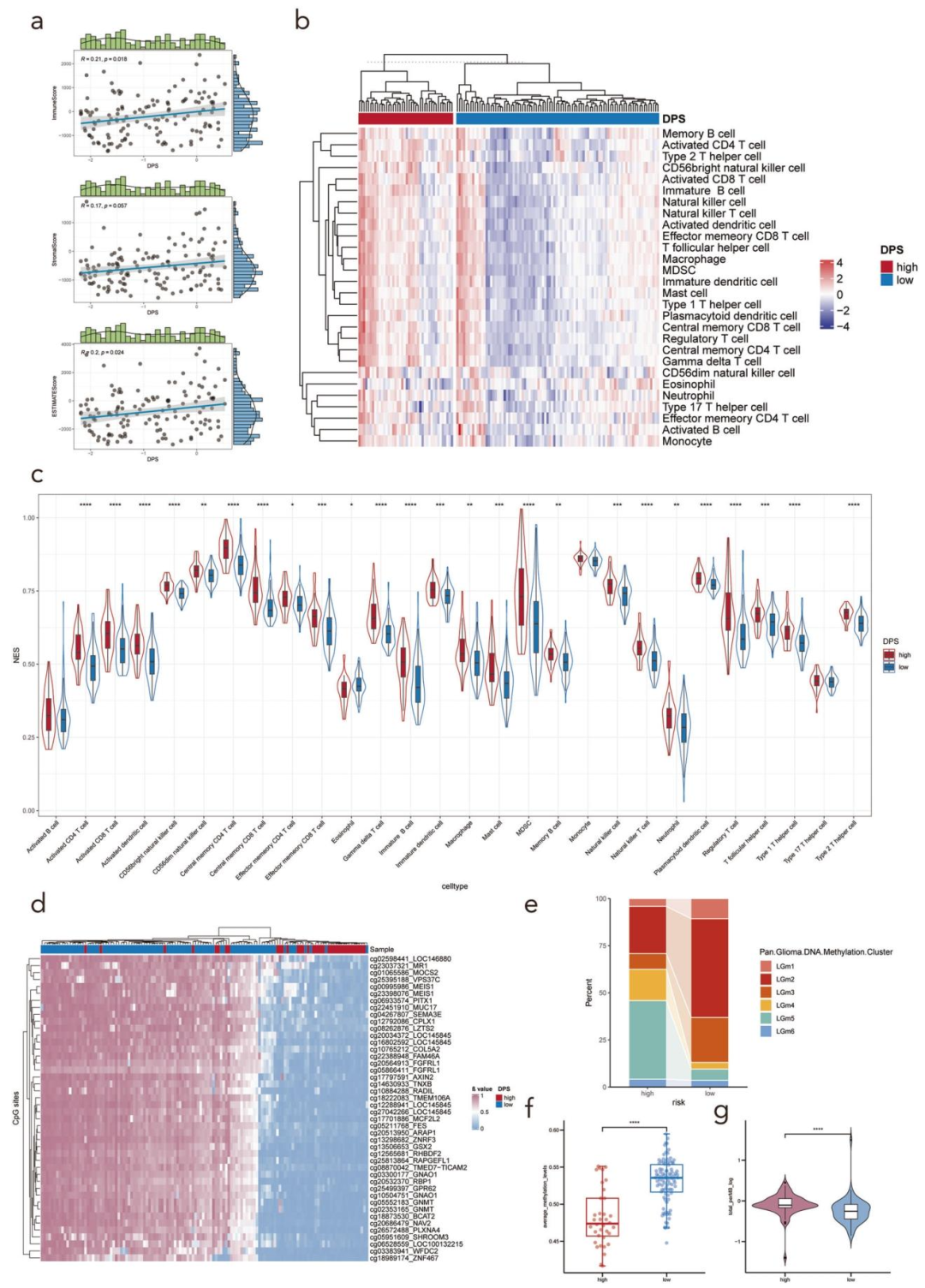
图 6:DPS与免疫浸润、表观遗传特征及TMB的关系图
a 基于ESTIMATE算法计算的免疫评分和估计评分与DPS显著相关。b 基于单样本基因集富集分析(ssGSEA)得到的高、低DPS亚型中28种免疫细胞亚群的浸润水平。c 采用ssGSEA计算细胞丰度评分,并在两个亚型间进行比较。统计显著性标注:***p<0.001;**p<0.01;*p<0.05。d 热图展示DNA甲基化变异性最高的44个CpG位点的β值。e 箱线图展示基于DNA甲基化的TCGA明确亚型在DPS亚组中的分布情况。f 不同DPS亚组间的平均甲基化水平存在差异。g 小提琴图展示不同DPS亚组间TMB的差异。
05
研究结论
该研究成功开发并验证了一种端到端多任务深度学习(MDL)模型,能够仅基于术前MRI图像,同时精准预测胶质瘤的关键分子特征(IDH突变状态、1p/19q共缺失状态)、组织学分级及患者预后。模型在多个内外验证队列中表现出稳定的高性能,其中预测分子与分级任务的AUC达0.710–0.903,预后预测的C指数在TCGA和UCSF队列中分别为0.723与0.671。研究进一步构建了深度预后评分(DPS),成功将患者分层为低DPS与高DPS亚型,其中高DPS与更差的生存结局显著相关。通过整合多组学分析,研究揭示了DPS评分背后的生物学基础:高DPS亚型与活化的致癌通路(如EMT、血管生成)、免疫热表型、更高的肿瘤突变负荷(TMB)、特定的蛋白质表达谱(如EGFR/HER2高表达)以及较低的肿瘤-间质比(TSR)密切相关。这些发现不仅提升了模型的可解释性,还为个体化治疗策略提供了潜在方向,例如针对不同DPS亚型推荐靶向药物。该研究为胶质瘤的无创、全面评估与预后分层提供了兼具高准确性、生物可解释性及临床转化潜力的新型工具。
参考文献:Wu X, Zhang S, Zhang Z, He Z, Xu Z, Wang W, Jin Z, You J, Guo Y, Zhang L, Huang W, Wang F, Liu X, Yan D, Cheng J, Yan J, Zhang S, Zhang B. Biologically interpretable multi-task deep learning pipeline predicts molecular alterations, grade, and prognosis in glioma patients. NPJ Precis Oncol. 2024 Aug 16;8(1):181. doi: 10.1038/s41698-024-00670-2.

AtomGit 是由开放原子开源基金会联合 CSDN 等生态伙伴共同推出的新一代开源与人工智能协作平台。平台坚持“开放、中立、公益”的理念,把代码托管、模型共享、数据集托管、智能体开发体验和算力服务整合在一起,为开发者提供从开发、训练到部署的一站式体验。
更多推荐
 已为社区贡献15条内容
已为社区贡献15条内容





所有评论(0)